| 2025年11月7日 DeepSpaceDB: 空間トランスクリプトミクス解析データベースを公開 |
DeepSpaceDB: a spatial transcriptomics atlas for interactive in-depth analysis of tissues and tissue microenvironments
Nucleic Acids Research, 2025 Oct 29 : gkaf1117.
https://doi.org/10.1093/nar/gkaf1117
Vladyslav Honcharuk1,2, Afeefa Zainab1, Yoshiya Horimoto3,4, Keiko Takemoto1, Diego Diez5, Shinpei Kawaoka1,6, Alexis Vandenbon*1,7,8
1 Institute for Life and Medical Sciences, Kyoto University
2 Department of Neuroscience, Graduate School of Medicine, Kyoto University
3 Department of Breast Surgery and Oncology, Tokyo Medical University Hospital
4 Department of Human Pathology, Juntendo University Faculty of Medicine
5 Immunology Frontier Research Center, Osaka University
6 Department of Integrative Bioanalytics, Institute of Development, Aging and Cancer (IDAC), Tohoku University
7 Institute for Liberal Arts and Sciences, Kyoto University
8 Department of Mammalian Regulatory Network, Graduate School of Biostudies, Kyoto University
*Corresponding Author
概要
本研究では、空間トランスクリプトミクスのための次世代データベース DeepSpaceDB(http://www.deepspacedb.com)を開発しました。空間トランスクリプトミクスは、組織内の遺伝子発現を詳細にマッピングし、細胞・分子プロセスの空間的な配置を明らかにします。しかし、そのデータ生成には高コストがかかり、解析には高度なバイオインフォマティクス知識が必要とされる上、既存のデータベースはインタラクティブな探索や解析の機能が限定的です。
DeepSpaceDB は、10x Genomics Visium データセットを中心に、高品質で使いやすいプラットフォームを提供することで、これらの課題に対応します。幅広いプラットフォーム網羅を重視するデータベースとは異なり、DeepSpaceDB は解析の深さとインタラクティブ性を重視しています。ユーザーは空間遺伝子発現を柔軟に探索し、サンプル内の複数領域を比較したりできます。
本プラットフォームでは、品質指標、データベース全体の概要、ズーム可能なプロットやホバー表示などのインタラクティブな可視化機能を提供します。さらに、これらの機能はユーザーがアップロードした Visium データにも適用でき、公開データを超えたカスタム解析が可能です。
高度な解析と直感的な操作性を統合した DeepSpaceDB は、組織構造や疾患生物学への理解を深める強力なリソースとなります。
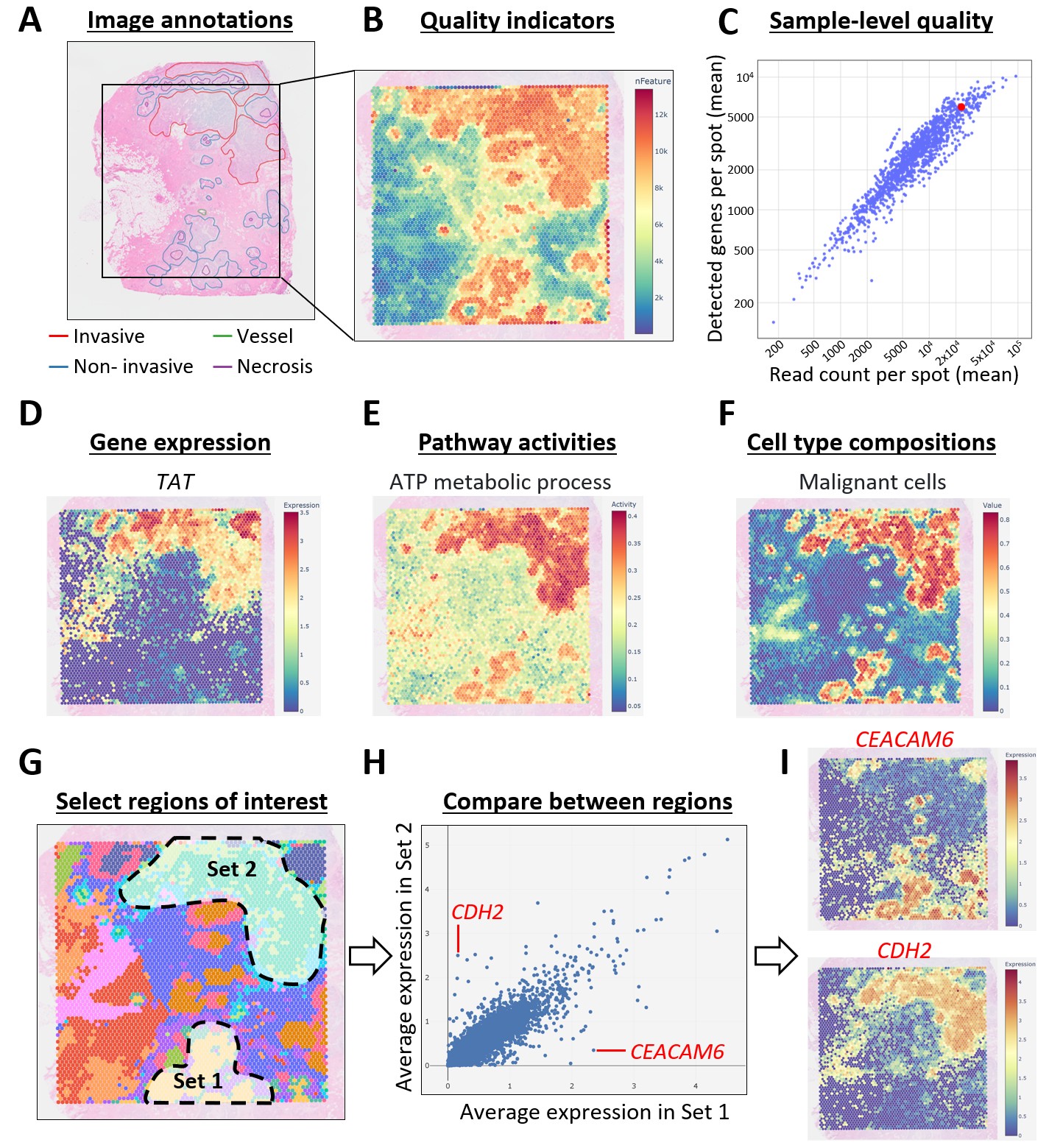
下図は DeepSpaceDB の機能の概要です。
(A) 一部の画像には病理医によるアノテーションが付与されています。
(B) スライドごとの品質(例:スポットごとの検出遺伝子数)を確認できます。
(C) 品質指標はデータベース内の他サンプルとの比較も可能です。
(D–E) 遺伝子発現パターンや経路活性を容易に可視化できます。
(F) 全スポットの細胞種組成が推定されています。
(G–H) ユーザーは任意の領域をインタラクティブに選択し、その平均遺伝子発現を算出できます。
(I) 選択領域間で大きく異なる遺伝子(CEACAM6、CDH2)の例を示します。